生細胞イメージングによりとらえるクロマチンの修飾および遺伝子発現の活性化
2018/02/27
木村 宏
(東京工業大学科学技術創成研究院 細胞制御工学研究センター)
email:木村 宏
領域融合レビュー, 7, e002 (2018) DOI: 10.7875/leading.author.7.e002
Hiroshi Kimura: Visualizing chromatin modification and gene activation by live cell imaging.

近年,蛍光顕微鏡による解析により生きた細胞において転写のダイナミクスをとらえることが可能になってきた.MS2系などを用いたRNAの可視化により特定のRNAの転写が定量的に解析され,エンハンサーを介した転写の活性化は断続的に起こることが示された.また,RNAポリメラーゼIIの1分子解析により多数のRNAポリメラーゼIIが一時的に1箇所に集積するようすが観察された.一方,転写の断続性が必ずしも明確な遺伝子発現のオンとオフの状態に分かれるとはかぎらず,転写の活性化について普遍的な機構の解明にはいたっていない.ヒストンの修飾は遺伝子発現の制御に重要な役割をはたすと考えられるが,最近,ヒストン修飾に特異的な抗体に由来する蛍光プローブを用いた解析により,ヒストンH3のアセチル化がRNAポリメラーゼIIによる転写の開始から伸長への移行を促進することが示された.今後,ゲノムを可視化する技術,転写産物を可視化する技術,翻訳後修飾を可視化する技術などを組み合わせることにより,発生や分化にともなうクロマチンの構造の変化および転写の活性化の機構をとらえることができるようになることが期待される.
遺伝子発現の制御は発生や分化,環境応答などの生命現象の鍵になる.すなわち,遺伝子の発現が,いつ,どこで,どのように起こるのかを明らかにすることは,生命現象の理解にとり非常に重要な課題のひとつである.特定の細胞における遺伝子発現の状態,すなわち,細胞に存在する転写産物やタンパク質の種類および量は,これまで,細胞の集団を用いて解析されていた.しかし,近年のめざましい技術開発により,単一の細胞を対象としたトランスクリプトーム解析なども可能になってきた1,2).また,ゲノムにおけるヒストンの修飾などクロマチンの状態や高次構造もChIP-seq法やHi-C法などの技術により解析が可能になり,核の構造および機能を1細胞のレベルで理解しようという気運も高まっている3).ただし,一般にエピゲノム解析やトランスクリプトーム解析は定常な状態におけるクロマチンの修飾やRNAの存在量の評価であり,また,同一の細胞におけるクロマチン構造や遺伝子発現の経時的な変化は追跡できない.そのため,遺伝子発現のダイナミクスの解析において核という場での物理化学的な性質を含めた転写制御の実体を解明するには,顕微鏡を用いた生細胞の解析が必須である.現在,顕微鏡による解析はゲノムの解析と比べ解像度やスループットの低いことは否めないが,近年,顕微鏡装置,プローブ,画像解析などの技術が着実かつ加速度的に進歩しており3),転写制御の機構の解明も進んでいる.このレビューにおいては,生細胞における遺伝子発現の活性化の解析から明らかにされてきたことを,翻訳後修飾のイメージングによる結果を中心に解説する.
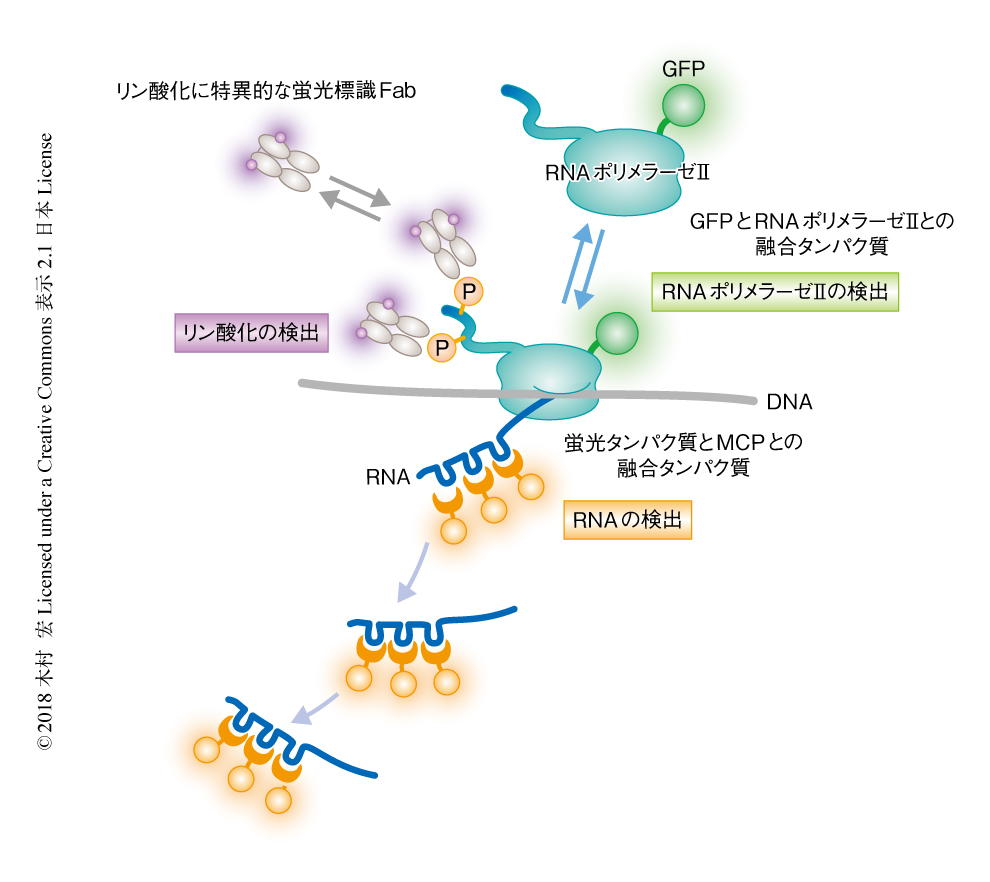
遺伝子発現のダイナミクスは,転写産物であるRNAの検出や転写装置であるRNAポリメラーゼIIなどのタンパク質の動態の追跡により解析されている(図1).通常,特定のRNAの検出には,タンパク質と結合するタグを付加したRNAを発現する配列をゲノムに組み込み,そのRNAと結合するタンパク質と蛍光タンパク質との融合タンパク質を発現させる.もっともよく用いられているのは,MS2ファージのコートタンパク質であるMCPとそれが結合するステムループの組合せである4).ステムループをくり返し配列として多コピーもたせることにより,転写されたRNAが蛍光の輝点として検出される.近年,蛍光タンパク質と融合したTALE(transcription activator-like effector)やヌクレアーゼ活性をもたないdCas9とガイドRNAを用いて特定のDNA配列を生細胞において検出する系も開発され,DNAとRNAを同時に可視化することもできるようになった5,6).
このMS2系を用いた転写産物の検出により,エンハンサーを介した転写の活性化は断続的に起こることが明らかにされた7)(新着論文レビュー でも掲載).つまり,活性化された遺伝子の転写は持続的に起こるのではなく,RNAポリメラーゼIIがつぎつぎと活性化される状態がパルス状に起こる.このような現象は“転写バースト”とよばれており,動物細胞やショウジョウバエに共通してみられる8).ただし,細胞性粘菌においてアクチン遺伝子の転写を理論モデルとあわせて詳細に解析した結果,転写は明確な転写バーストのオンとオフの2つの状態により説明されるのではなく,転写開始の頻度の連続的な変化をともなうことが示唆されている9).また,プロモーターにおけるTATAボックスの変異は転写開始の頻度を低下させるがオンとオフのスイッチにはそれほど影響しないことも示された.したがって,転写の量はエンハンサーの強度による転写バーストの発生頻度のみならず,プロモーターの配列などに依存して連続的に制御されるとも考えられる.MS2系による転写の活性化のキネティクスの解析の例は限られていることもあり,転写制御の一般性と多様性についての理解は今後の課題である.また,転写の活性化のキネティクスを制御する因子の実体については明らかにされていない.
一方,転写を担うRNAポリメラーゼIIの可視化によっても転写のダイナミクスは解析されている.GFPとRNAポリメラーゼIIとの融合タンパク質は細胞において機能的であることは,温度感受性変異株の相補やRNAポリメラーゼIIの阻害剤であるαアマニチンに対する耐性変異体による相補などにより確認されているため,GFPとRNAポリメラーゼIIとの融合タンパク質の動態は内在性のRNAポリメラーゼIIと類似すると考えられる10).しかし,多くの培養細胞において複数のRNAポリメラーゼIIが集積する転写部位は数千箇所もあり,しかも,転写反応しているRNAポリメラーゼIIはすべてのRNAポリメラーゼIIのうち約30%にすぎないことから,バルクのGFPとRNAポリメラーゼIIとの融合タンパク質の観察では転写部位の同定や詳細なダイナミクスを解析することは困難であった11).しかし,近年,1分子イメージングにより転写開始の際に多数のRNAポリメラーゼIIが一過性に集積するようすが観察された12,13).これは,転写バーストとも一致する観察であり,複数のRNAポリメラーゼIIが遺伝子に一過性にロードされることが示唆される.最近,タンパク質やRNAの集合した構造がまわりの環境と相分離を起こし,このことが細胞機能の制御にはたらく可能性が注目されているが14),この局所的な分子の集合も一種の相分離である可能性が示唆されている.このような相分離がタンパク質複合体の形成を促進し転写の活性化にはたらくとすれば,非常に興味深い.
遺伝子の転写を担うRNAポリメラーゼIIは多くのサブユニットから構成されるタンパク質複合体である.その最大のサブユニットであるRPB1は,N末端側のポリメラーゼ触媒ドメインにくわえ,7アミノ酸残基Tyr-Ser-Pro-Thr-Ser-Pro-Serのくり返し配列から構成されるC末端ドメインをもつ.このくり返し配列のSerはRNAポリメラーゼIIの活性化の状態に応じてリン酸化されることが知られており,転写開始前複合体のRNAポリメラーゼIIは非リン酸化型であるが,転写開始のときにはTFIIHによりSer5が,転写伸長のときにはP-TEFbによりSer2が,それぞれリン酸化される15).そのため,Serのリン酸化に特異的な抗体を用いることにより特定の状態のRNAポリメラーゼIIを検出できる.最近,これらの特異的な抗体を用いて,生細胞において特定の状態のRNAポリメラーゼIIのみを検出することが可能になった.この翻訳後修飾に特異的な抗体を用いた生細胞イメージングの技術は,ヒストンの修飾に対し開発されたものであり,ヒストンの修飾とRNAポリメラーゼIIの修飾を同時に可視化することにより,生細胞における遺伝子発現の活性化におけるヒストン修飾の役割が明らかにされた16).
転写の制御においては,DNAに直接に結合する転写因子にくわえ,クロマチンの構造が重要な役割をはたす.クロマチン構造の標識としては,シトシンのメチル化やヒドロキシメチル化などのDNAの修飾,ヌクレオソームを形成するヒストンの種類(バリアント)および修飾,クロマチンと結合するRNA,などが知られている.また,クロマチンの高次構造の構築には,DNAをつなぐコヒーシンなどのタンパク質,また,転写そのものが関与する.クロマチンの高次構造は近接するゲノムの領域を同定するHi-C法などにより解析されているが,この解析には細胞の固定が必要なため,顕微鏡レベルでのダイナミクスの解析にはいたっていない.一方,生細胞におけるヒストン修飾のダイナミクスの解析はプローブの開発とともに進んでいる.
生細胞におけるヒストン修飾の動態を解析するため,いくつかのプローブが開発されている17,18).ひとつは,FRET(fluorescence resonance energy transfer,蛍光共鳴エネルギー移動)やルシフェラーゼの相補性を利用したセンサーであり,センサー自体の修飾の状態に依存したFRETやルシフェラーゼ活性の変化を検出する.すなわち,センサーに修飾部位およびその修飾に依存的なタンパク質結合ドメインをもたせることにより,分子構造の変化にともない2つの蛍光分子の位置が変化することによるFRETやルシフェラーゼ活性を検出する.したがって,これらのセンサーを用いることにより,ヒストン修飾酵素と脱ヒストン修飾酵素のバランスを生細胞において核の全体あるいはクロマチンにて追跡することが可能である.しかしながら,これらのセンサーは内在性のヒストン修飾は検出できないため,転写の活性化あるいは抑制にともなう局所的なクロマチンの動態の追跡にはむかない.それに対して,翻訳後修飾に特異的な抗体をもとに作製されたプローブは内在性のヒストン修飾の検出に適している(図2).
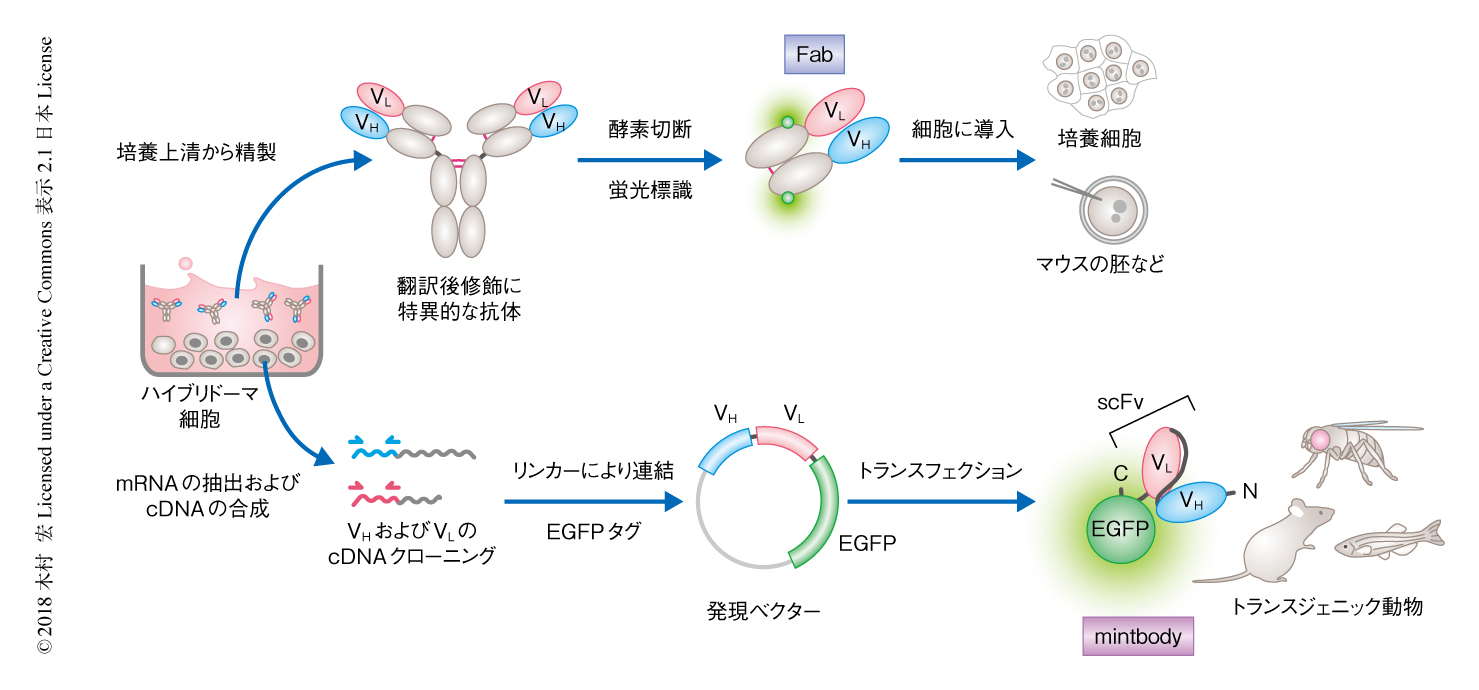
翻訳後修飾に特異的な抗体から開発されたプローブとして,抗原結合断片(Fab)および修飾に特異的な細胞内抗体(modification-specific intracellular antibody:mintbody)がある.Fabはほとんどのモノクローナル抗体から調製することができ,かつ,任意の蛍光色素により標識できるという利点があるが,マイクロインジェクションなど物理的な方法により細胞に導入する必要がある.一方,mintbodyは遺伝子にコードされているためDNAトランスフェクションにより簡便に発現させることができる.しかし,細胞において機能的な抗体を発現させることは容易ではなく,ほとんどの場合,タンパク質の折りたたみや安定性に問題が生じ細胞質において凝集体を形成したり分解をうけたりする.これは,抗体はもともと酸化環境の小胞体において合成され,分子内および分子間のS-S結合を形成して細胞外に分泌されるのに対し,mintbodyは還元状態の細胞質において抗体の一部分のみが合成されるものであり,構造の高い安定性がもとめられる.mintbodyの安定性はわずか1アミノ酸残基の置換により大きく影響されることがわかっており,安定な抗体の探索や既存の抗体の改変が検討されている19).
生細胞に対する抗体の使用については,抗原への結合による機能の阻害が懸念される.しかしながら,2価の結合部位をもち抗原に対する結合親和性の高い通常の免疫グロブリンGとは異なり,Fabやmintbodyは1価の結合部位しかもたないため結合親和性が低く,また,細胞においてはほかのタンパク質とも競合する.光による蛍光退色による解析から,これらのプローブが抗原と結合している時間は1秒以下から数十秒であり,適度の量であれば阻害は限定的であると考えられる.実際,Fabやmintbodyが存在しても培養細胞の増殖は影響されず,また,胚の発生や分化にも影響しないことが示されており,これらのプローブを用いることにより生細胞においてヒストン修飾やRNAポリメラーゼの翻訳後修飾を追跡することが可能になっている20).
遺伝子発現の活性化におけるRNAポリメラーゼIIのダイナミクスとヒストン修飾との関係について,生細胞におけるグルココルチコイドによる転写の誘導系を用いて解析された16).グルココルチコイドによる転写の誘導の鍵となる転写因子はグルココルチコイド受容体である.グルココルチコイド受容体は,グルココルチコイドの非存在下においては細胞質に局在するが,グルココルチコイドと結合するとすみやかに核に移行し,標的となるDNA配列と結合して転写を活性化する.モデル細胞として,グルココルチコイド誘導性のマウス乳がんウイルスのプロモーターにより制御される遺伝子をゲノムの1箇所にタンデムに約200コピー挿入したMMTVアレイをもち,かつ,GFPとグルココルチコイド受容体との融合タンパク質を発現するマウスの繊維芽細胞を用いた.グルココルチコイド受容体の標的となる遺伝子はゲノムに多く存在するため,蛍光顕微鏡による通常の観察では単一遺伝子座において転写因子およびRNAポリメラーゼIIの活性化を検出することは困難であるが,MMTVアレイにはグルココルチコイド受容体の顕著な集積がみられるため,ダイナミクスの解析が比較的容易である.このモデル細胞に,転写開始型であるSer5のリン酸化したRNAポリメラーゼII,転写伸長型であるSer2のリン酸化したRNAポリメラーゼII,非リン酸化型のRNAポリメラーゼIIをそれぞれ認識する蛍光標識Fabを導入し,グルココルチコイドを添加してMMTVアレイにおけるグルココルチコイド受容体およびRNAポリメラーゼIIの集積を測定した.この結果をキネティックモデルにフィッティングしたところ,転写因子であるグルココルチコイド受容体が集積したのち,約1分でRNAポリメラーゼIIが集積し,さらに1分後には転写が開始し,その2分後に転写の伸長にいたることが明らかにされた.
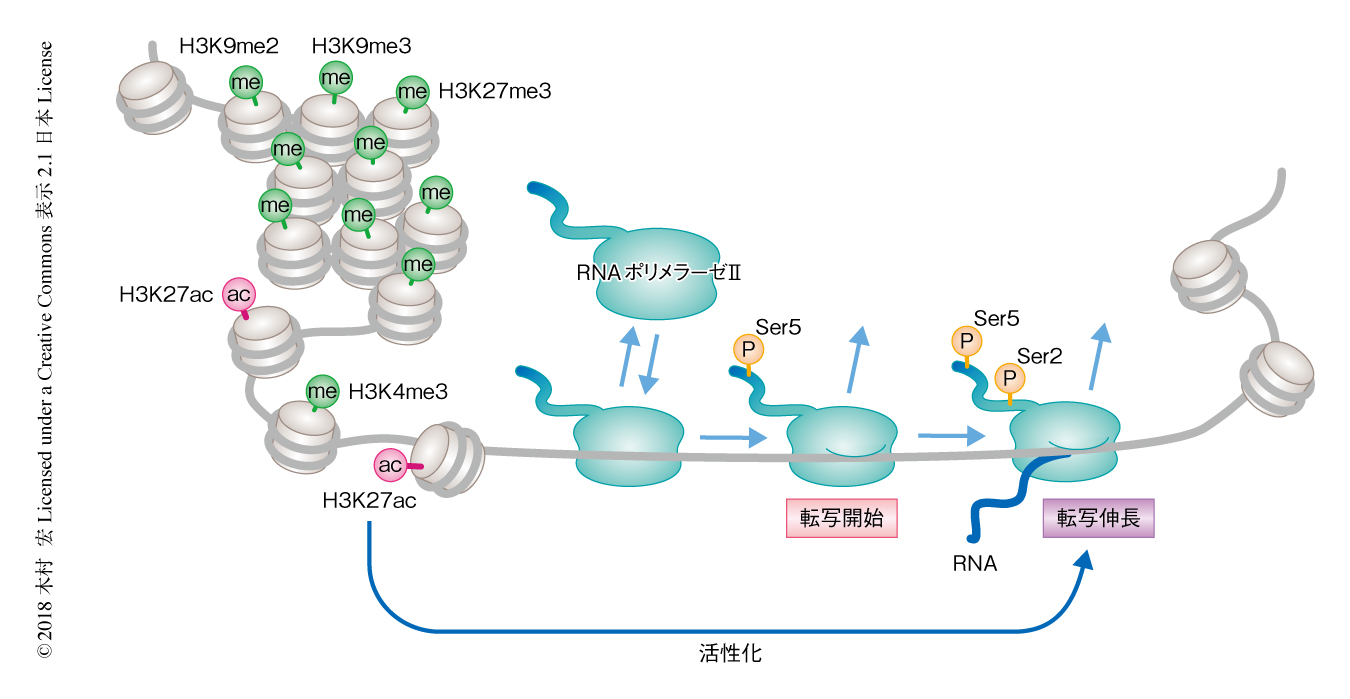
MMTVアレイにおけるヒストン修飾をみたところ,転写開始点の付近にみられるヒストンH3のLys4のジメチル化およびトリメチル化は,グルココルチコイドの添加のまえからすでに存在した.それに対し,ヒストンH3のLys27のアセチル化については細胞により大きな差がみられた.そこで,MMTVアレイにおいてヒストンH3のLys27のアセチル化のレベルが高い細胞と低い細胞についてRNAポリメラーゼIIのキネティクスを解析したところ,ヒストンH3のLys27のアセチル化のレベルが高い細胞においては,転写因子であるグルココルチコイド受容体の結合の促進にくわえ,転写の開始から伸長への移行も促進されていることが明らかにされた(図3).
細胞膜に受容体が存在するペプチド型のホルモンとは異なり,ステロイドホルモンのひとつであるグルココルチコイドは細胞に浸透し転写因子であるグルココルチコイド受容体と直接に結合してすみやかに転写を誘導する.実際,培養細胞のモデル系においては,グルココルチコイドを培地に添加したのち10分程度で転写にまでいたる.しかしながら,転写因子が結合してから,RNAポリメラーゼIIの結合,転写開始,転写伸長のおのおのの過程において,1分~2分の時間を要していた.とくに,転写の開始から伸長にいたる過程は比較的長かったことから,ヒストンのアセチル化により転写の開始から伸長への移行が促進されることは迅速な転写の誘導において意義があることと思われた.その分子機構としては,ブロモドメインをもちアセチル化したヒストンH3のLys27と直接に結合するBrd4やp300が,転写伸長にはたらく複合体SECと結合することが考えられた.
グルココルチコイドにより転写の誘導される遺伝子は転写の活性化にはたらくヒストン修飾を保持しており,グルココルチコイドのはたらきによりすみやかに転写が誘導される.しかし,発生や分化,ストレス応答の際に発現が活性化される遺伝子は,必ずしも転写の活性化が準備されているわけではなく,抑制型のヒストン修飾を保持していることも多い.今後,これらの遺伝子の転写の活性化の際にヒストン修飾やクロマチン構造がどのように変化し,その変化がどのように転写にはたらくのかを明らかにする必要がある.その際,MMTVアレイのような人工的かつ多コピーの遺伝子ではなく,内在性の単一遺伝子座における転写の活性化を調べることが重要であると考えられる.MS2系においてはRNAのくり返し配列に複数のGFPとMS2の融合タンパク質が結合するため単一の転写産物の検出が可能であるが,単一遺伝子座の可視化やタンパク質の動態の解析にはさらなる技術の開発が必要になる.単一遺伝子座の可視化には,TALEやCRISPR-dCas9を利用した手法のほか,parB遺伝子とその結合配列を用いた系なども開発されており21),MS2系や翻訳後修飾のイメージングと組み合わせることにより,遺伝子発現の活性化におけるクロマチン構造の役割や動態を明らかにすることが可能になると思われる.
また,将来的には生細胞イメージングとエピゲノムの統合的な解析,および,遺伝学的な手法を用いた転写制御にはたらくおのおののタンパク質の役割の解明が必要だと思われる.理想的には,生細胞イメージングを実施した細胞においてエピゲノム解析やHi-C法による解析を実施することにより,時間的な変化や核における局在をふまえたうえでのゲノム情報を取得することでイメージングとゲノム解析の融合が可能になると考えられ,その手法の開発が待たれる.また,クロマチンの高次構造が転写におよぼす影響の解析には,人工的に制御の可能なゲノム配列の利用やコヒーシンなどクロマチン構造の構築にはたらくタンパク質の除去が有効である.ノックアウトやノックダウンはRNAレベルでの制御であるため,タンパク質の除去は必ずしも迅速ではない.そのため,遺伝子の発現に影響がみられた場合においても,タンパク質の除去による直接の効果なのか2次的な影響なのかを区別できないことがある.最近,オーキシン誘導デグロンを用いたタンパク質の分解系が普及しはじめ,迅速なタンパク質の除去が可能になりつつある22).オーキシン誘導デグロン法とイメージングによる解析とを組み合わせることにより,遺伝子発現の活性化の分子機構の解明に近づくことができると考えられる.
略歴:1996年 北海道大学大学院理学研究科にて博士号取得,同年 英国Oxford大学 博士研究員,2002年 東京医科歯科大学難治疾患研究所 助教授,2003年 京都大学大学院医学研究科 特任教授,2007年 大阪大学大学院生命機能研究科 准教授を経て,2014年より東京工業大学科学技術創成研究院 教授.
研究テーマ:核とクロマチンの機能および構造.
関心事:イメージングとゲノム解析の融合.
研究室URL:http://kimura-lab.bio.titech.ac.jp/index.html
© 2018 木村 宏 Licensed under CC 表示 2.1 日本
(東京工業大学科学技術創成研究院 細胞制御工学研究センター)
email:木村 宏
領域融合レビュー, 7, e002 (2018) DOI: 10.7875/leading.author.7.e002
Hiroshi Kimura: Visualizing chromatin modification and gene activation by live cell imaging.
要 約
近年,蛍光顕微鏡による解析により生きた細胞において転写のダイナミクスをとらえることが可能になってきた.MS2系などを用いたRNAの可視化により特定のRNAの転写が定量的に解析され,エンハンサーを介した転写の活性化は断続的に起こることが示された.また,RNAポリメラーゼIIの1分子解析により多数のRNAポリメラーゼIIが一時的に1箇所に集積するようすが観察された.一方,転写の断続性が必ずしも明確な遺伝子発現のオンとオフの状態に分かれるとはかぎらず,転写の活性化について普遍的な機構の解明にはいたっていない.ヒストンの修飾は遺伝子発現の制御に重要な役割をはたすと考えられるが,最近,ヒストン修飾に特異的な抗体に由来する蛍光プローブを用いた解析により,ヒストンH3のアセチル化がRNAポリメラーゼIIによる転写の開始から伸長への移行を促進することが示された.今後,ゲノムを可視化する技術,転写産物を可視化する技術,翻訳後修飾を可視化する技術などを組み合わせることにより,発生や分化にともなうクロマチンの構造の変化および転写の活性化の機構をとらえることができるようになることが期待される.
はじめに
遺伝子発現の制御は発生や分化,環境応答などの生命現象の鍵になる.すなわち,遺伝子の発現が,いつ,どこで,どのように起こるのかを明らかにすることは,生命現象の理解にとり非常に重要な課題のひとつである.特定の細胞における遺伝子発現の状態,すなわち,細胞に存在する転写産物やタンパク質の種類および量は,これまで,細胞の集団を用いて解析されていた.しかし,近年のめざましい技術開発により,単一の細胞を対象としたトランスクリプトーム解析なども可能になってきた1,2).また,ゲノムにおけるヒストンの修飾などクロマチンの状態や高次構造もChIP-seq法やHi-C法などの技術により解析が可能になり,核の構造および機能を1細胞のレベルで理解しようという気運も高まっている3).ただし,一般にエピゲノム解析やトランスクリプトーム解析は定常な状態におけるクロマチンの修飾やRNAの存在量の評価であり,また,同一の細胞におけるクロマチン構造や遺伝子発現の経時的な変化は追跡できない.そのため,遺伝子発現のダイナミクスの解析において核という場での物理化学的な性質を含めた転写制御の実体を解明するには,顕微鏡を用いた生細胞の解析が必須である.現在,顕微鏡による解析はゲノムの解析と比べ解像度やスループットの低いことは否めないが,近年,顕微鏡装置,プローブ,画像解析などの技術が着実かつ加速度的に進歩しており3),転写制御の機構の解明も進んでいる.このレビューにおいては,生細胞における遺伝子発現の活性化の解析から明らかにされてきたことを,翻訳後修飾のイメージングによる結果を中心に解説する.
1.RNAの可視化による生細胞における転写制御の解析
遺伝子発現のダイナミクスは,転写産物であるRNAの検出や転写装置であるRNAポリメラーゼIIなどのタンパク質の動態の追跡により解析されている(図1).通常,特定のRNAの検出には,タンパク質と結合するタグを付加したRNAを発現する配列をゲノムに組み込み,そのRNAと結合するタンパク質と蛍光タンパク質との融合タンパク質を発現させる.もっともよく用いられているのは,MS2ファージのコートタンパク質であるMCPとそれが結合するステムループの組合せである4).ステムループをくり返し配列として多コピーもたせることにより,転写されたRNAが蛍光の輝点として検出される.近年,蛍光タンパク質と融合したTALE(transcription activator-like effector)やヌクレアーゼ活性をもたないdCas9とガイドRNAを用いて特定のDNA配列を生細胞において検出する系も開発され,DNAとRNAを同時に可視化することもできるようになった5,6).
このMS2系を用いた転写産物の検出により,エンハンサーを介した転写の活性化は断続的に起こることが明らかにされた7)(新着論文レビュー でも掲載).つまり,活性化された遺伝子の転写は持続的に起こるのではなく,RNAポリメラーゼIIがつぎつぎと活性化される状態がパルス状に起こる.このような現象は“転写バースト”とよばれており,動物細胞やショウジョウバエに共通してみられる8).ただし,細胞性粘菌においてアクチン遺伝子の転写を理論モデルとあわせて詳細に解析した結果,転写は明確な転写バーストのオンとオフの2つの状態により説明されるのではなく,転写開始の頻度の連続的な変化をともなうことが示唆されている9).また,プロモーターにおけるTATAボックスの変異は転写開始の頻度を低下させるがオンとオフのスイッチにはそれほど影響しないことも示された.したがって,転写の量はエンハンサーの強度による転写バーストの発生頻度のみならず,プロモーターの配列などに依存して連続的に制御されるとも考えられる.MS2系による転写の活性化のキネティクスの解析の例は限られていることもあり,転写制御の一般性と多様性についての理解は今後の課題である.また,転写の活性化のキネティクスを制御する因子の実体については明らかにされていない.
2.RNAポリメラーゼIIの可視化による生細胞における転写制御の解析
一方,転写を担うRNAポリメラーゼIIの可視化によっても転写のダイナミクスは解析されている.GFPとRNAポリメラーゼIIとの融合タンパク質は細胞において機能的であることは,温度感受性変異株の相補やRNAポリメラーゼIIの阻害剤であるαアマニチンに対する耐性変異体による相補などにより確認されているため,GFPとRNAポリメラーゼIIとの融合タンパク質の動態は内在性のRNAポリメラーゼIIと類似すると考えられる10).しかし,多くの培養細胞において複数のRNAポリメラーゼIIが集積する転写部位は数千箇所もあり,しかも,転写反応しているRNAポリメラーゼIIはすべてのRNAポリメラーゼIIのうち約30%にすぎないことから,バルクのGFPとRNAポリメラーゼIIとの融合タンパク質の観察では転写部位の同定や詳細なダイナミクスを解析することは困難であった11).しかし,近年,1分子イメージングにより転写開始の際に多数のRNAポリメラーゼIIが一過性に集積するようすが観察された12,13).これは,転写バーストとも一致する観察であり,複数のRNAポリメラーゼIIが遺伝子に一過性にロードされることが示唆される.最近,タンパク質やRNAの集合した構造がまわりの環境と相分離を起こし,このことが細胞機能の制御にはたらく可能性が注目されているが14),この局所的な分子の集合も一種の相分離である可能性が示唆されている.このような相分離がタンパク質複合体の形成を促進し転写の活性化にはたらくとすれば,非常に興味深い.
3.RNAポリメラーゼIIの翻訳後修飾
遺伝子の転写を担うRNAポリメラーゼIIは多くのサブユニットから構成されるタンパク質複合体である.その最大のサブユニットであるRPB1は,N末端側のポリメラーゼ触媒ドメインにくわえ,7アミノ酸残基Tyr-Ser-Pro-Thr-Ser-Pro-Serのくり返し配列から構成されるC末端ドメインをもつ.このくり返し配列のSerはRNAポリメラーゼIIの活性化の状態に応じてリン酸化されることが知られており,転写開始前複合体のRNAポリメラーゼIIは非リン酸化型であるが,転写開始のときにはTFIIHによりSer5が,転写伸長のときにはP-TEFbによりSer2が,それぞれリン酸化される15).そのため,Serのリン酸化に特異的な抗体を用いることにより特定の状態のRNAポリメラーゼIIを検出できる.最近,これらの特異的な抗体を用いて,生細胞において特定の状態のRNAポリメラーゼIIのみを検出することが可能になった.この翻訳後修飾に特異的な抗体を用いた生細胞イメージングの技術は,ヒストンの修飾に対し開発されたものであり,ヒストンの修飾とRNAポリメラーゼIIの修飾を同時に可視化することにより,生細胞における遺伝子発現の活性化におけるヒストン修飾の役割が明らかにされた16).
4.生細胞における翻訳後修飾の可視化
転写の制御においては,DNAに直接に結合する転写因子にくわえ,クロマチンの構造が重要な役割をはたす.クロマチン構造の標識としては,シトシンのメチル化やヒドロキシメチル化などのDNAの修飾,ヌクレオソームを形成するヒストンの種類(バリアント)および修飾,クロマチンと結合するRNA,などが知られている.また,クロマチンの高次構造の構築には,DNAをつなぐコヒーシンなどのタンパク質,また,転写そのものが関与する.クロマチンの高次構造は近接するゲノムの領域を同定するHi-C法などにより解析されているが,この解析には細胞の固定が必要なため,顕微鏡レベルでのダイナミクスの解析にはいたっていない.一方,生細胞におけるヒストン修飾のダイナミクスの解析はプローブの開発とともに進んでいる.
生細胞におけるヒストン修飾の動態を解析するため,いくつかのプローブが開発されている17,18).ひとつは,FRET(fluorescence resonance energy transfer,蛍光共鳴エネルギー移動)やルシフェラーゼの相補性を利用したセンサーであり,センサー自体の修飾の状態に依存したFRETやルシフェラーゼ活性の変化を検出する.すなわち,センサーに修飾部位およびその修飾に依存的なタンパク質結合ドメインをもたせることにより,分子構造の変化にともない2つの蛍光分子の位置が変化することによるFRETやルシフェラーゼ活性を検出する.したがって,これらのセンサーを用いることにより,ヒストン修飾酵素と脱ヒストン修飾酵素のバランスを生細胞において核の全体あるいはクロマチンにて追跡することが可能である.しかしながら,これらのセンサーは内在性のヒストン修飾は検出できないため,転写の活性化あるいは抑制にともなう局所的なクロマチンの動態の追跡にはむかない.それに対して,翻訳後修飾に特異的な抗体をもとに作製されたプローブは内在性のヒストン修飾の検出に適している(図2).
翻訳後修飾に特異的な抗体から開発されたプローブとして,抗原結合断片(Fab)および修飾に特異的な細胞内抗体(modification-specific intracellular antibody:mintbody)がある.Fabはほとんどのモノクローナル抗体から調製することができ,かつ,任意の蛍光色素により標識できるという利点があるが,マイクロインジェクションなど物理的な方法により細胞に導入する必要がある.一方,mintbodyは遺伝子にコードされているためDNAトランスフェクションにより簡便に発現させることができる.しかし,細胞において機能的な抗体を発現させることは容易ではなく,ほとんどの場合,タンパク質の折りたたみや安定性に問題が生じ細胞質において凝集体を形成したり分解をうけたりする.これは,抗体はもともと酸化環境の小胞体において合成され,分子内および分子間のS-S結合を形成して細胞外に分泌されるのに対し,mintbodyは還元状態の細胞質において抗体の一部分のみが合成されるものであり,構造の高い安定性がもとめられる.mintbodyの安定性はわずか1アミノ酸残基の置換により大きく影響されることがわかっており,安定な抗体の探索や既存の抗体の改変が検討されている19).
生細胞に対する抗体の使用については,抗原への結合による機能の阻害が懸念される.しかしながら,2価の結合部位をもち抗原に対する結合親和性の高い通常の免疫グロブリンGとは異なり,Fabやmintbodyは1価の結合部位しかもたないため結合親和性が低く,また,細胞においてはほかのタンパク質とも競合する.光による蛍光退色による解析から,これらのプローブが抗原と結合している時間は1秒以下から数十秒であり,適度の量であれば阻害は限定的であると考えられる.実際,Fabやmintbodyが存在しても培養細胞の増殖は影響されず,また,胚の発生や分化にも影響しないことが示されており,これらのプローブを用いることにより生細胞においてヒストン修飾やRNAポリメラーゼの翻訳後修飾を追跡することが可能になっている20).
5.生細胞におけるヒストン修飾によるRNAポリメラーゼIIの制御の解析
遺伝子発現の活性化におけるRNAポリメラーゼIIのダイナミクスとヒストン修飾との関係について,生細胞におけるグルココルチコイドによる転写の誘導系を用いて解析された16).グルココルチコイドによる転写の誘導の鍵となる転写因子はグルココルチコイド受容体である.グルココルチコイド受容体は,グルココルチコイドの非存在下においては細胞質に局在するが,グルココルチコイドと結合するとすみやかに核に移行し,標的となるDNA配列と結合して転写を活性化する.モデル細胞として,グルココルチコイド誘導性のマウス乳がんウイルスのプロモーターにより制御される遺伝子をゲノムの1箇所にタンデムに約200コピー挿入したMMTVアレイをもち,かつ,GFPとグルココルチコイド受容体との融合タンパク質を発現するマウスの繊維芽細胞を用いた.グルココルチコイド受容体の標的となる遺伝子はゲノムに多く存在するため,蛍光顕微鏡による通常の観察では単一遺伝子座において転写因子およびRNAポリメラーゼIIの活性化を検出することは困難であるが,MMTVアレイにはグルココルチコイド受容体の顕著な集積がみられるため,ダイナミクスの解析が比較的容易である.このモデル細胞に,転写開始型であるSer5のリン酸化したRNAポリメラーゼII,転写伸長型であるSer2のリン酸化したRNAポリメラーゼII,非リン酸化型のRNAポリメラーゼIIをそれぞれ認識する蛍光標識Fabを導入し,グルココルチコイドを添加してMMTVアレイにおけるグルココルチコイド受容体およびRNAポリメラーゼIIの集積を測定した.この結果をキネティックモデルにフィッティングしたところ,転写因子であるグルココルチコイド受容体が集積したのち,約1分でRNAポリメラーゼIIが集積し,さらに1分後には転写が開始し,その2分後に転写の伸長にいたることが明らかにされた.
MMTVアレイにおけるヒストン修飾をみたところ,転写開始点の付近にみられるヒストンH3のLys4のジメチル化およびトリメチル化は,グルココルチコイドの添加のまえからすでに存在した.それに対し,ヒストンH3のLys27のアセチル化については細胞により大きな差がみられた.そこで,MMTVアレイにおいてヒストンH3のLys27のアセチル化のレベルが高い細胞と低い細胞についてRNAポリメラーゼIIのキネティクスを解析したところ,ヒストンH3のLys27のアセチル化のレベルが高い細胞においては,転写因子であるグルココルチコイド受容体の結合の促進にくわえ,転写の開始から伸長への移行も促進されていることが明らかにされた(図3).
細胞膜に受容体が存在するペプチド型のホルモンとは異なり,ステロイドホルモンのひとつであるグルココルチコイドは細胞に浸透し転写因子であるグルココルチコイド受容体と直接に結合してすみやかに転写を誘導する.実際,培養細胞のモデル系においては,グルココルチコイドを培地に添加したのち10分程度で転写にまでいたる.しかしながら,転写因子が結合してから,RNAポリメラーゼIIの結合,転写開始,転写伸長のおのおのの過程において,1分~2分の時間を要していた.とくに,転写の開始から伸長にいたる過程は比較的長かったことから,ヒストンのアセチル化により転写の開始から伸長への移行が促進されることは迅速な転写の誘導において意義があることと思われた.その分子機構としては,ブロモドメインをもちアセチル化したヒストンH3のLys27と直接に結合するBrd4やp300が,転写伸長にはたらく複合体SECと結合することが考えられた.
おわりに
グルココルチコイドにより転写の誘導される遺伝子は転写の活性化にはたらくヒストン修飾を保持しており,グルココルチコイドのはたらきによりすみやかに転写が誘導される.しかし,発生や分化,ストレス応答の際に発現が活性化される遺伝子は,必ずしも転写の活性化が準備されているわけではなく,抑制型のヒストン修飾を保持していることも多い.今後,これらの遺伝子の転写の活性化の際にヒストン修飾やクロマチン構造がどのように変化し,その変化がどのように転写にはたらくのかを明らかにする必要がある.その際,MMTVアレイのような人工的かつ多コピーの遺伝子ではなく,内在性の単一遺伝子座における転写の活性化を調べることが重要であると考えられる.MS2系においてはRNAのくり返し配列に複数のGFPとMS2の融合タンパク質が結合するため単一の転写産物の検出が可能であるが,単一遺伝子座の可視化やタンパク質の動態の解析にはさらなる技術の開発が必要になる.単一遺伝子座の可視化には,TALEやCRISPR-dCas9を利用した手法のほか,parB遺伝子とその結合配列を用いた系なども開発されており21),MS2系や翻訳後修飾のイメージングと組み合わせることにより,遺伝子発現の活性化におけるクロマチン構造の役割や動態を明らかにすることが可能になると思われる.
また,将来的には生細胞イメージングとエピゲノムの統合的な解析,および,遺伝学的な手法を用いた転写制御にはたらくおのおののタンパク質の役割の解明が必要だと思われる.理想的には,生細胞イメージングを実施した細胞においてエピゲノム解析やHi-C法による解析を実施することにより,時間的な変化や核における局在をふまえたうえでのゲノム情報を取得することでイメージングとゲノム解析の融合が可能になると考えられ,その手法の開発が待たれる.また,クロマチンの高次構造が転写におよぼす影響の解析には,人工的に制御の可能なゲノム配列の利用やコヒーシンなどクロマチン構造の構築にはたらくタンパク質の除去が有効である.ノックアウトやノックダウンはRNAレベルでの制御であるため,タンパク質の除去は必ずしも迅速ではない.そのため,遺伝子の発現に影響がみられた場合においても,タンパク質の除去による直接の効果なのか2次的な影響なのかを区別できないことがある.最近,オーキシン誘導デグロンを用いたタンパク質の分解系が普及しはじめ,迅速なタンパク質の除去が可能になりつつある22).オーキシン誘導デグロン法とイメージングによる解析とを組み合わせることにより,遺伝子発現の活性化の分子機構の解明に近づくことができると考えられる.
文 献
- Clark, S. J., Lee, H. J., Smallwood, S. A. et al.: Single-cell epigenomics: powerful new methods for understanding gene regulation and cell identity. Genome Biol., 17, 72 (2016)[PubMed]
- Kelsey, G., Stegle, O. & Reik, W.: Single-cell epigenomics: recording the past and predicting the future. Science, 358, 69-75 (2017)[PubMed]
- Dekker, J., Belmont, A. S., Guttman, M. et al.: The 4D nucleome project. Nature, 549, 219-226 (2017)[PubMed]
- Vera, M., Biswas, J., Senecal, A. et al.: Single-cell and single-molecule analysis of gene expression regulation. Annu. Rev. Genet., 50, 267-291 (2016)[PubMed]
- Miyanari, Y., Ziegler-Birling, C. & Torres-Padilla, M. E.: Live visualization of chromatin dynamics with fluorescent TALEs. Nat. Struct. Mol. Biol., 20, 1321-1324 (2013)[PubMed]
- Ochiai, H., Sugawara, T. & Yamamoto, T.: Simultaneous live imaging of the transcription and nuclear position of specific genes. Nucleic Acids Res., 43, e127 (2015)[PubMed]
- Fukaya, T., Lim, B. & Levine, M.: Enhancer control of transcriptional bursting. Cell, 166, 358-368 (2016)[PubMed] [新着論文レビュー]
- Bartman, C. R., Hsu, S. C., Hsiung, C. C. et al.: Enhancer regulation of transcriptional bursting parameters revealed by forced chromatin looping. Mol. Cell, 62, 237-247 (2016)[PubMed]
- Corrigan, A. M., Tunnacliffe, E., Cannon, D. et al.: A continuum model of transcriptional bursting. Elife, 5, e13051 (2016)[PubMed]
- Sugaya, K., Vigneron, M. & Cook, P. R.: Mammalian cell lines expressing functional RNA polymerase II tagged with the green fluorescent protein. J. Cell Sci., 113, 2679-2683 (2000)[PubMed]
- Kimura, H., Sugaya, K. & Cook, P. R.: The transcription cycle of RNA polymerase II in living cells. J. Cell Biol., 159, 777-782 (2002)[PubMed]
- Cisse, I. I., Izeddin, I., Causse, S. Z. et al.: Real-time dynamics of RNA polymerase II clustering in live human cells. Science, 341, 664-667 (2013)[PubMed]
- Cho, W. K., Jayanth, N., English, B. P. et al.: RNA Polymerase II cluster dynamics predict mRNA output in living cells. Elife, 5, e13617 (2016)[PubMed]
- Hymanm, A. A., Weber, C. A. & Julicher, F.: Liquid-liquid phase separation in biology. Annu. Rev. Cell Dev. Biol., 30, 39-58 (2014)[PubMed]
- Harlen, K. M. & Churchman, L. S.: The code and beyond: transcription regulation by the RNA polymerase II carboxy-terminal domain. Nat. Rev. Mol. Cell Biol., 18, 263-273 (2017)[PubMed]
- Stasevich, T. J., Hayashi-Takanaka, Y., Sato, Y. et al.: Regulation of RNA polymerase II activation by histone acetylation in single living cells. Nature, 516, 272-275 (2014)[PubMed]
- Kimura, H., Hayashi-Takanaka, Y., Stasevich, T. J. et al.: Visualizing posttranslational and epigenetic modifications of endogenous proteins in vivo. Histochem. Cell Biol., 144, 101-109 (2015)[PubMed]
- Lyon, K. & Stasevich, T. J.: Imaging translational and post-translational gene regulatory dynamics in living cells with antibody-based probes. Trends Genet., 33, 322-335 (2017)[PubMed]
- Sato, Y., Kujirai, T., Arai, R. et al.: A genetically encoded probe for live-cell imaging of H4K20 monomethylation. J. Mol. Biol., 428, 3885-3902 (2016)[PubMed]
- Hayashi-Takanaka, Y., Yamagata, K., Wakayama, T. et al.: Tracking epigenetic histone modifications in single cells using Fab-based live endogenous modification labeling. Nucleic Acids Res., 39, 6475-6488 (2011)[PubMed]
- Germier, T., Kocanova, S., Walther, N. et al.: Real-time imaging of a single gene reveals transcription-initiated local confinement. Biophys. J., 113, 1383-1394 (2017)[PubMed]
- Natsume, T. & Kanemaki, M. T.: Conditional degrons for controlling protein expression at the protein level. Annu. Rev. Genet., 51, 83-102 (2017)[PubMed]
著者プロフィール
略歴:1996年 北海道大学大学院理学研究科にて博士号取得,同年 英国Oxford大学 博士研究員,2002年 東京医科歯科大学難治疾患研究所 助教授,2003年 京都大学大学院医学研究科 特任教授,2007年 大阪大学大学院生命機能研究科 准教授を経て,2014年より東京工業大学科学技術創成研究院 教授.
研究テーマ:核とクロマチンの機能および構造.
関心事:イメージングとゲノム解析の融合.
研究室URL:http://kimura-lab.bio.titech.ac.jp/index.html
© 2018 木村 宏 Licensed under CC 表示 2.1 日本